大家好,我是东哥。
之前一直在分享pandas的一些骚操作:pandas骚操作,根据大家反映还不错,但是很多技巧都混在了一起,没有细致的分类,这样不利于查找,也不成体系。
利用闲暇之余将有关数据清洗、数据分析的一些技能再次进行分类,里面也包含了我平时用到的一些小技巧,此次就从数据清洗缺失值处理走起,链接:pandas数据清洗,关注这个话题可第一时间看到更新。
所有数据和代码可在我的GitHub获取:
https://github.com/xiaoyusmd/PythonDataScience
如有帮助,求个star!
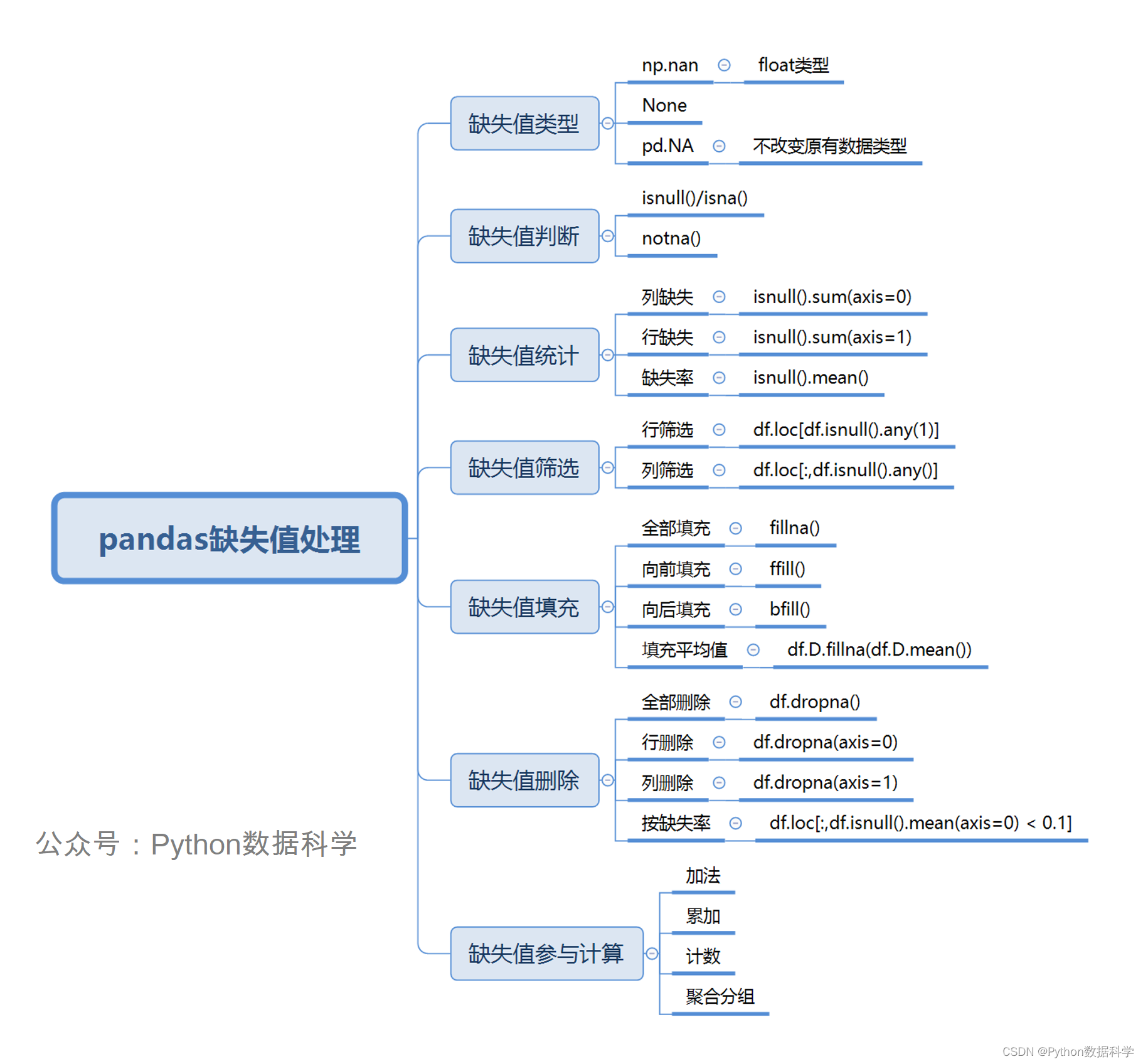
一、缺失值类型
在pandas中,缺失数据显示为NaN。缺失值有3种表示方法,np.nan,none,pd.NA。
1、np.nan
缺失值有个特点(坑),它不等于任何值,连自己都不相等。如果用nan和任何其它值比较都会返回nan。
np.nan == np.nan
>> False
也正由于这个特点,在数据集读入以后,不论列是什么类型的数据,默认的缺失值全为np.nan。
因为nan在Numpy中的类型是浮点,因此整型列会转为浮点;而字符型由于无法转化为浮点型,只能归并为object类型(‘O’),原来是浮点型的则类型不变。
type(np.nan)
>> float
pd.Series([1,2,3]).dtype
>> dtype('int64')
pd.Series([1,np.nan,3]).dtype
>> dtype('float64')
初学者做数据处理遇见object类型会发懵,不知道这是个啥,明明是字符型,导入后就变了,其实是因为缺失值导致的。
除此之外,还要介绍一种针对时间序列的缺失值,它是单独存在的,用NaT表示,是pandas的内置类型,可以视为时间序列版的np.nan,也是与自己不相等。
s_time = pd.Series([pd.Timestamp('20220101')]*3)
s_time
>> 0 2022-01-01
1 2022-01-01
2 2022-01-01
dtype:datetime64[ns]
-----------------
s_time[2] = pd.NaT
s_time
>> 0 2022-01-01
1 2022-01-01
2 NaT
dtype:datetime64[ns]
2、None
还有一种就是None,它要比nan好那么一点,因为它至少自己与自己相等。
None == None
>> True
在传入数值类型后,会自动变为np.nan。
type(pd.Series([1,None])[1])
>> numpy.float64
只有当传入object类型时是不变的,因此可以认为如果不是人工命名为None的话,它基本不会自动出现在pandas中,所以None大家基本也看不到。
type(pd.Series([1,None],dtype='O')[1])
>> NoneType
3、NA标量
pandas1.0以后的版本中引入了一个专门表示缺失值的标量pd.NA,它代表空整数、空布尔值、空字符,这个功能目前处于实验阶段。
开发者也注意到了这点,对于不同数据类型采取不同的缺失值表示会很乱。pd.NA就是为了统一而存在的。
pd.NA的目标是提供一个缺失值指示器,可以在各种数据类型中一致使用(而不是np.nan、None或者NaT分情况使用)。
s_new = pd.Series([1, 2], dtype="Int64")
s_new
>> 0 1
1 2
dtype: Int64
-----------------
s_new[1] = pd.NaT
s_new
>> 0 1
1 <NA>
dtype: Int64
同理,对于布尔型、字符型一样不会改变原有数据类型,这样就解决了原来动不动就变成object类型的麻烦了。
下面是pd.NA的一些常用算术运算和比较运算的示例:
##### 算术运算
# 加法
pd.NA + 1
>> <NA>
-----------
# 乘法
"a" * pd.NA
>> <NA>
-----------
# 以下两种其中结果为1
pd.NA ** 0
>> 1
-----------
1 ** pd.NA
>> 1
##### 比较运算
pd.NA == pd.NA
>> <NA>
-----------
pd.NA < 2.5
>> <NA>
-----------
np.log(pd.NA)
>> <NA>
-----------
np.add(pd.NA, 1)
>> <NA>
二、缺失值判断
了解了缺失值的几种形式后,我们要知道如何判断缺失值。对于一个dataframe而言,判断缺失的主要方法就是isnull()或者isna(),这两个方法会直接返回True和False的布尔值。可以是对整个dataframe或者某个列。
df = pd.DataFrame({
'A':['a1','a1','a2','a3'],
'B':['b1',None,'b2','b3'],
'C':[1,2,3,4],
'D':[5,None,9,10]})
# 将无穷设置为缺失值
pd.options.mode.use_inf_as_na = True
1、对整个dataframe判断缺失
df.isnull()
>> A B C D
0 False False False False
1 False True False True
2 False False False False
3 False False False False
2、对某个列判断缺失
df['C'].isnull()
>> 0 False
1 False
2 False
3 False
Name: C, dtype: bool
如果想取非缺失可以用notna(),使用方法是一样的,结果相反。
三、缺失值统计
1、列缺失
一般我们会对一个dataframe的列进行缺失统计,查看每个列有多少缺失,如果缺失率过高再进行删除或者插值等操作。那么直接在上面的isnull()返回的结果上直接应用.sum()即可,axis默认等于0,0是列,1是行。
## 列缺失统计
isnull().sum(axis=0)
2、行缺失
但是很多情况下,我们也需要对行进行缺失值判断。比如一行数据可能一个值都没有,如果这个样本进入模型,会造成很大的干扰。因此,行列两个缺失率通常都要查看并统计。
操作很简单,只需要在sum()中设置axis=1即可。
## 行缺失统计
isnull().sum(axis=1)
3、缺失率
有时我不仅想要知道缺失的数量,我更想知道缺失的比例,即缺失率。正常可能会想到用上面求得数值再比上总行数。但其实这里有个小技巧可以一步就实现。
## 缺失率
df.isnull().sum(axis=0)/df.shape[0]
## 缺失率(一步到位)
isnull().mean()
四、缺失值筛选
筛选需要loc配合完成,对于行和列的缺失筛选如下:
# 筛选有缺失值的行
df.loc[df.isnull().any(1)]
>> A B C D
1 a1 None 2 NaN
-----------------
# 筛选有缺失值的列
df.loc[:,df.isnull().any()]
>> B D
0 b1 5.0
1 None NaN
2 b2 9.0
3 b3 10.0
如果要查询没有缺失值的行和列,可以对表达式用取反~操作:
df.loc[~(df.isnull().any(1))]
>> A B C D
0 a1 b1 1 5.0
2 a2 b2 3 9.0
3 a3 b3 4 10.0
上面使用了any判断只要有缺失就进行筛选,也可以用all判断是否全部缺失,同样可以对行里进行判断,如果整列或者整行都是缺失值,那么这个变量或者样本就失去了分析的意义,可以考虑删除。
五、缺失值填充
一般我们对缺失值有两种处理方法,一种是直接删除,另外一种是保留并填充。下面先介绍填充的方法fillna。
# 将dataframe所有缺失值填充为0
df.fillna(0)
>> A B C D
0 a1 b1 1 5.0
1 a1 0 2 0.0
2 a2 b2 3 9.0
3 a3 b3 4 10.0
--------------
# 将D列缺失值填充为-999
df.D.fillna('-999')
>> 0 5
1 -999
2 9
3 10
Name: D, dtype: object
方法很简单,但使用时需要注意一些参数。
- inplace:可以设置
fillna(0, inplace=True)来让填充生效,原dataFrame被填充。 - methond:可以设置
methond方法来实现向前或者向后填充,pad/ffill为向前填充,bfill/backfill为向后填充,比如df.fillna(methond='ffill'),也可以简写为df.ffill()。
df.ffill()
>> A B C D
0 a1 b1 1 5.0
1 a1 b1 2 5.0
2 a2 b2 3 9.0
3 a3 b3 4 10.0
原缺失值都会按照前一个值来填充(B列1行,D列1行)。
除了用前后值来填充,也可以用整个列的均值来填充,比如对D列的其它非缺失值的平均值8来填充缺失值。
df.D.fillna(df.D.mean())
>> 0 5.0
1 8.0
2 9.0
3 10.0
Name: D, dtype: float64
六、缺失值删除
删除缺失值也非情况,比如是全删除还是删除比较高缺失率,这个要看自己的容忍程度,真实的数据必然会存在缺失的,这个无法避免。而且缺失在某些情况下也代表了一定的含义,要视情况而定。
1、全部直接删除
# 全部直接删除
df.dropna()
>> A B C D
0 a1 b1 1 5.0
2 a2 b2 3 9.0
3 a3 b3 4 10.0
2、行缺失删除
# 行缺失删除
df.dropna(axis=0)
>> A B C D
0 a1 b1 1 5.0
2 a2 b2 3 9.0
3 a3 b3 4 10.0
3、列缺失删除
# 列缺失删除
df.dropna(axis=1)
>> A C
0 a1 1
1 a1 2
2 a2 3
3 a3 4
-------------
# 删除指定列范围内的缺失,因为C列无缺失,所以最后没有变化
df.dropna(subset=['C'])
>> A B C D
0 a1 b1 1 5.0
1 a1 None 2 NaN
2 a2 b2 3 9.0
3 a3 b3 4 10.0
4、按缺失率删除
这个可以考虑用筛选的方法来实现,比如要删除列缺失大于0.1的(即筛选小于0.1的)。
df.loc[:,df.isnull().mean(axis=0) < 0.1]
>> A C
0 a1 1
1 a1 2
2 a2 3
3 a3 4
-------------
# 删除行缺失大于0.1的
df.loc[df.isnull().mean(axis=1) < 0.1]
>> A B C D
0 a1 b1 1 5.0
2 a2 b2 3 9.0
3 a3 b3 4 10.0
七、缺失值参与计算
如果不对缺失值处理,那么缺失值会按照什么逻辑进行计算呢?
下面我们一起看一下各种运算下缺失值的参与逻辑。
1、加法
df
>>A B C D
0 a1 b1 1 5.0
1 a1 None 2 NaN
2 a2 b2 3 9.0
3 a3 b3 4 10.0
---------------
# 对所有列求和
df.sum()
>> A a1a1a2a3
C 10
D 24
可以看到,加法是会忽略缺失值的。
2、累加
# 对D列进行累加
df.D.cumsum()
>> 0 5.0
1 NaN
2 14.0
3 24.0
Name: D, dtype: float64
---------------
df.D.cumsum(skipna=False)
>> 0 5.0
1 NaN
2 NaN
3 NaN
Name: D, dtype: float64
cumsum累加会忽略NA,但值会保留在列中,可以使用skipna=False跳过有缺失值的计算并返回缺失值。
3、计数
# 对列计数
df.count()
>> A 4
B 3
C 4
D 3
dtype: int64
缺失值不进入计数范围里。
4、聚合分组
df.groupby('B').sum()
>> C D
B
b1 1 5.0
b2 3 9.0
b3 4 10.0
---------------
df.groupby('B',dropna=False).sum()
>> C D
B
b1 1 5.0
b2 3 9.0
b3 4 10.0
NaN 2 0.0
聚合时会默认忽略缺失值,如果要缺失值计入到分组里,可以设置dropna=False。这个用法和其它比如value_counts是一样的,有的时候需要看缺失值的数量。
以上就是所有关于缺失值的常用操作了,从理解缺失值的3种表现形式开始,到缺失值判断、统计、处理、计算等。
原创不易,欢迎点赞、在看支持。
参考:
[1]深入浅出pandas
[2]https://mp.weixin.qq.com/s/Ool5T49RxYj-Os4DWzTeyQ
原创文章持续更新,系列文章可以微信搜一搜「 Python数据科学」第一时间阅读。